












Prezados participantes do curso: “Produtos de Oceanogradia por Satélite – Conceitos, Acesso e Processamento”, segue abaixo o link do “notebook” interativo do Google Colab com as atividades do curso.

Este “notebook” interativo contém instruções para a instalação das ferramentas necessárias para a criação de scripts Python e a manipulação dos dados mostrados no curso. Todas as instruções e scripts são executados na nuvem, não sendo necessário instalar as ferramentas e baixar arquivos localmente, como no procedimento pré-curso. Para executar as instruções, clicar no ícone “Play” entre colchetes à esquerda de cada célula.
Para ter uma melhor experiência com a ferramenta e poder editar / salvar seus scripts, é imprescindível a criação de uma cópia no seu próprio Google Drive, em “Arquivo” -> “Salvar uma cópia no Drive”.
Seguem algumas orientações nas imagens abaixo (clique nas imagens para ampliar):
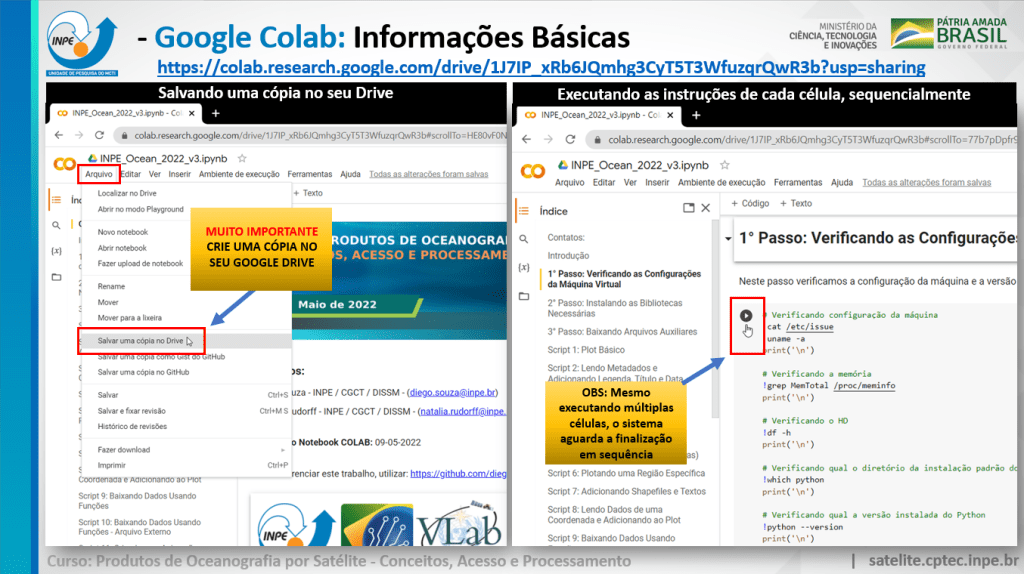



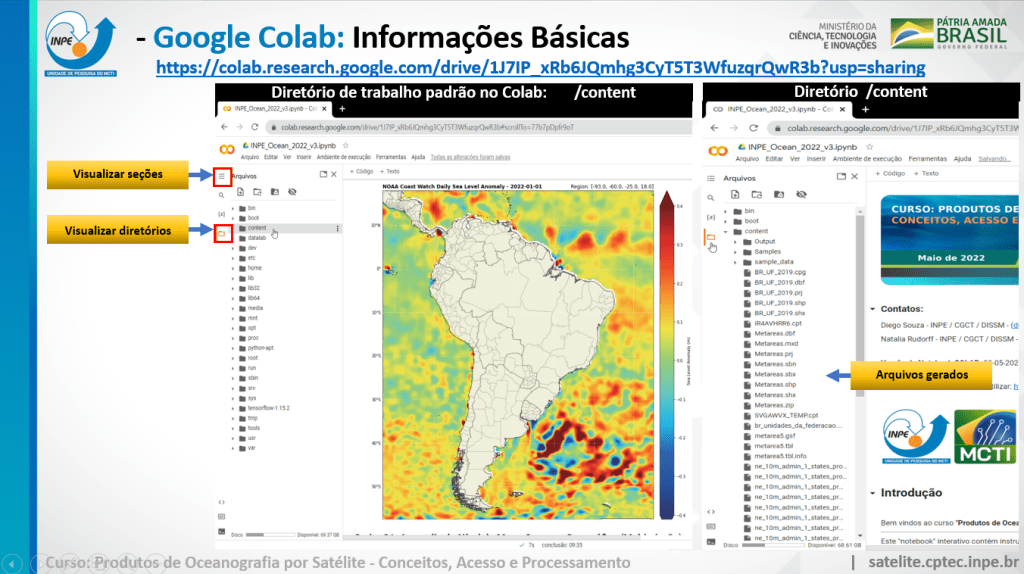
Nos vemos no curso!
Equipe VLAB – Brazil CoE – INPE


Atividade Pré-Curso – Produtos de Oceanografia por Satélite: Conceitos, Acesso e Processamento
Olá! Bem vindos à atividade pré-curso!
Contato: Em caso de dúvidas, enviar um e-mail para:
E-mail: [email protected]
Ao finalizar a atividade pré-curso, os participantes estarão capacitados a:
Durante o curso online dos dias 24, 26 e 31/05 vamos aprender também:
Duração estimada da atividade Pré-curso: 3:00 h
Abaixo, a estrutura das atividades práticas. Nesta atividade pré-curso veremos algumas operações mais básicas, que serão revisadas no dia 24/05. Já no tempo restante do dia 24/05 e nos dias 25 e 31/05, veremos novos conceitos.

Pré-requisito (desejável):
O conteúdo completo do curso pode ser acessado também neste blog:
Abaixo, algumas informações preliminares:
Ferramentas necessárias para o pré-curso:
Nesta atividade, utilizaremos as seguintes ferramentas:
Para os primeiros três itens acima (“Python 3.9”, “Gerenciador de Pacotes” e “Gerenciador de Ambientes Virtuais”), a ferramenta “Miniconda” será suficiente.
Como editor de texto ou IDE (ambiente de desenvolvimento integrado), existem muitas opções disponíveis (Gedit, Visual Studio Code, Spyder, PyCharm, Atom, Jupyter Notebooks, etc.), mas pela simplicidade, neste procedimento usaremos o “Notepad++” (ou “Notepadqq” no Linux).
Para obter amostras de produtos de oceanografia por satélite, vamos baixar dados de servidores FTP abertos da NOAA utilizando o software Filezilla.
Observação: Execução local x Execução na nuvem:
É possível executar os scripts Python que veremos tanto localmente (em seus próprios computadores) como na nuvem (na plataforma Google Colab por exemplo). Durante o treinamento, vamos exemplificar ambos! Neste procedimento pré-curso, veremos como instalar as ferramentas necessárias e executar os scripts localmente. Já durante o curso, veremos como executar os scripts na nuvem, sem a necessidade de instalação local. Assim os alunos terão uma visão geral de ambas as possibilidades.

Obs.: O procedimento mostrado a seguir foi realizado no Windows 10.
Com estas informações preliminares, mãos a obra!
Procedimento de instalação dos software necessários:
1) Faça o download e instale como administrador a ferramenta Miniconda para Python 3.9 (aproximadamente 60 MB) no seguinte link:
docs.conda.io/en/latest/miniconda.html

Nos seguintes links, você encontrará as instruções para instalação do Miniconda: Windows e Linux.
Observações (instalador Windows):
Observações (instalador Linux):
./Miniconda3-py39_4.11.0-Linux-x86_64.sh -p /meu_diretorio/
Observações (instalador Windows / Linux):
Agora que temos a ferramenta Miniconda instalada, vamos criar nosso ambiente virtual Python, que neste procedimento será chamado chamado “ocean” (Obs.: você pode dar qualquer nome ao ambiente virtual).
Criando um Ambiente Virtual Python e instalando bibliotecas:
2) Vamos criar um ambiente virtual Python chamado “ocean” e instalar as seguintes bibliotecas:
Obs: Nem todas as bibliotecas acima serão utilizadas na atividade pré-curso, mas já vamos deixar todas as bibliotecas instaladas para o curso online, caso o aluno deseje executar os scripts localmente.

No Windows: Para criar o ambiente virtual, abra o “Anaconda Prompt” recentemente instalado, como administrador:

No Linux: Não é necessário abrir o Anaconda Prompt, os comandos podem ser usados diretamente no terminal
Criando o Ambiente Virtual (env) Python
Para a criação do ambiente virtual, insira o seguinte comando:
conda create --name ocean -c conda-forge matplotlib cartopy imageio boto3 netcdf4 pyhdf gdal scipy pandas scikit-learn
Onde:
ocean: é o nome do seu ambiente virtual Python. Poderia ser qualquer nome, como “oceanografia”, “curso_oceano”, etc.
matplotlib cartopy imageio boto3 netcdf4 pyhdf gdal scipy pandas scikit-learn: as bibliotecas que desejamos instalar. Existem muitas outras bibliotecas disponíveis, estas são as que utilizaremos no treinamento.
Observações sobre a instalação das bibliotecas no ambiente:

A mensagem abaixo confirma a correta criação do ambiente virtual.

Obs.: “base” (visto entre parênteses na imagem acima) é o nome do ambiente padrão do conda, e não é recomendada sua utilização para a instalação de bibliotecas devido a possíveis conflitos entre versões. É uma boa prática criar ambientes específicos para aplicações específicas (como este treinamento por exemplo), tendo assim o maior controle sobre suas instalações.
Após o procedimento, ative o ambiente virtual “ocean” recém criado com o seguinte comando:
conda activate ocean
Observação: No Linux, você pode utilizar também o comando:
source activate ocean
Ao ativá-lo, você verá o nome “ocean” entre parênteses (ao invés de “base”). Isso significa que o ambiente “ocean” foi ativado corretamente.
Informações Adicionais sobre Ambientes Virtuais:
Comandos úteis do conda
Ainda que os seguintes comandos não sejam necessários para este treinamento, são muito úteis no desenvolvimento em geral:
Encontre mais informações sobre a gestão de ambientes virtuais neste link.
Estamos prontos para começar a programar com Python, no entanto, precisamos de um editor para escrever nosso código e também precisamos de produtos de oceanografia por satélite de amostra. Vamos ver como baixá-los!
Baixando um Editor de Textos:
3-) Existem diversas opções de editores ou IDE’s disponíveis para criação dos nossos scripts. Mas a título de simplicidade (e evitar que o aluno encontre problemas na configuração das opções de editores mais avançados), vamos utilizar o Notepad++. Falaremos mais sobre isso no treinamento online.
No Windows: Faça o download e instale o Notepad++ no seguinte link (apenas 4 MB):
notepad-plus-plus.org/downloads/

No Linux: Caso deseje, você pode instalar o Notepadqq com o seguinte comando:
sudo apt-get install notepadqq
Ou então usar o Gedit, ou outro editor Linux.
Observação:
Baixando Amostras de Produtos de Oceanografia por Satélite no formato NetCDF:
4-) Crie um diretório na sua máquina para os arquivos desta atividade. Neste procedimento exemplo utilizamos o diretório VLAB\Python\ (em: C:\VLAB\Python\). Este será nosso diretório de trabalho. Use o diretório que desejar.
Vamos baixar uma amostra de Temperatura da Superfície do Mar (TSM) diária no formato NetCDF, dos servidores FTP abertos da NOAA.
Para isso, vamos utilizar o software FileZilla, que pode ser baixado no seguinte link:
filezilla-project.org/download.php
FileZilla é uma solução FTP de código aberto gratuita.
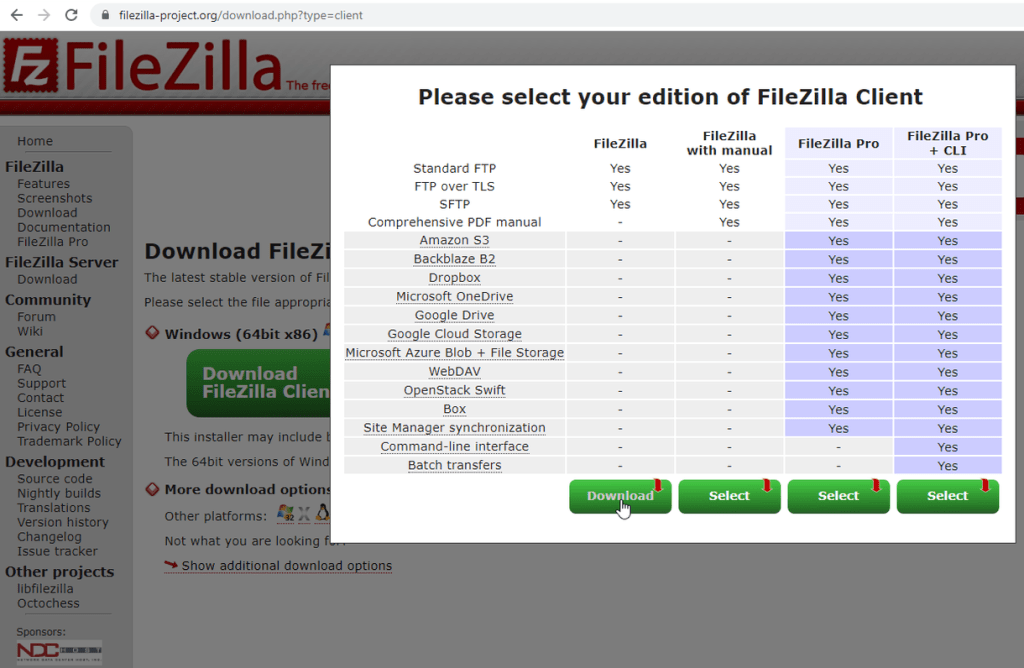
Baixe e instale a versão gratuita mais recente do FileZilla. Neste procedimento, a versão 3.59.0 foi utilizada.
Vamos baixar um arquivo global diário de TSM (5 km) do seguinte servidor FTP da NOAA:
ftp.star.nesdis.noaa.gov
Nosso arquivo de interesse está localizado no seguinte diretório:
/pub/socd/mecb/crw/data/5km/v3.1_op/nc/v1.0/daily/sst/2022
Execute o FileZilla. No campo “Host”, insira ftp.star.nesdis.noaa.gov e aperte Enter.
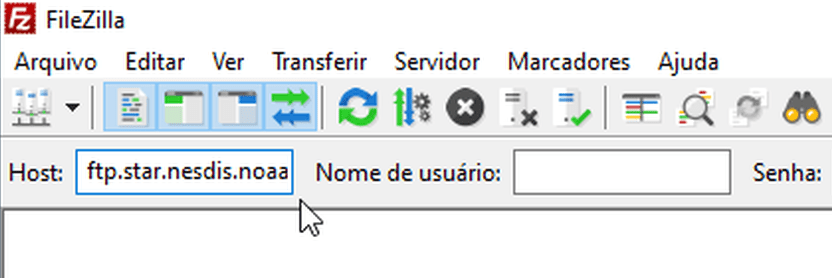
Aparecerá uma janela informando que o servidor não suporta FTP sobre TLS. Clique “OK”.

Após a conexão bem sucedida, em “Endereço remoto”, insira o seguinte diretório:
/pub/socd/mecb/crw/data/5km/v3.1_op/nc/v1.0/daily/sst/2022
Ao confirmar com um Enter, a lista de arquivos neste diretório será mostrada na parte inferior da interface:

Agora vamos escolher onde o FileZilla deverá salvar os arquivos baixados. Em “Endereço local”, escolha seu diretório de trabalho (neste procedimento exemplo, estamos utilizando C:\VLAB\Python. Selecione o seu diretório de trabalho.
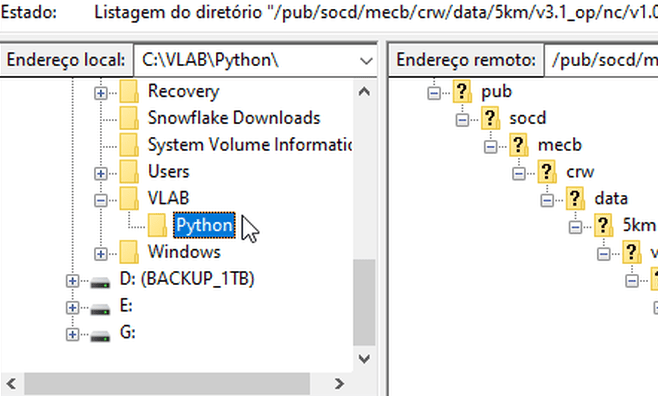
Neste procedimento, vamos baixar o arquivo “coraltemp_v3.1_20220101.nc”, que é um arquivo diário de TSM global (5km) do dia 01/01/2022.
Os arquivos diários de TSM global da NOAA possuem a seguinte nomenclatura:
coraltemp_v3.1_YYYYMMDD.nc
Onde: YYYY: ano , MM: mês e DD: dia
Para baixar o NetCDF desta data, clique com o botão direito sobre o arquivo e selecione “Baixar”:

O console do FileZilla irá mostrar o andamento do download (pasta de destino, porcentagem, entre outras informações):

Ao finalizar o download você verá uma mensagem no canto inferior direito indicando que o download foi completado:

E o arquivo baixado estará localizado na pasta escolhida como destino:

E assim baixamos nosso dado de amostra. Como vamos ver no curso, existem muitos links abertos de FTP da NOAA, com uma infinidade de dados disponíveis, que podem ser baixados de modo semelhante! No curso vamos ver também como fazer este mesmo procedimento, porém utilizando scripts, o que é muito mais simples e rápido.
Neste ponto já temos nosso ambiente de programação e nosso editor de texto instalados e uma amostra de dado disponível. Estamos prontos para iniciar! Vamos criar nosso primeiro script.
SCRIPT 1: PLOT BÁSICO
IMPORTANTE: Nesta atividade pré-curso não vamos explicar com muitos detalhes o que faz cada instrução. Os conceitos serão revisados e explicados com mais detalhes no curso online. O mais importante nessa etapa é conseguir executar os scripts sem maiores problemas.
Abra seu editor de texto ou IDE (neste procedimento, o “Notepad ++”), insira o código abaixo e salve-o como “script_01.py” no seu diretório de trabalho (C:\VLAB\Python\ , no nosso caso). Este é o mesmo diretório onde você baixou o arquivo NetCDF no passo anterior.
Importante: Na linha 12, insira o nome do arquivo NetCDF que você baixou no passo anterior. Caso tenha sido o arquivo do dia 01/01/2022, será o mesmo nome do exemplo a seguir.
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 1: Basic Plot | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(10,5)) | |
| # Plot the image | |
| plt.imshow(data, vmin=-2, vmax=35, origin='lower', cmap='jet') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_01.png') | |
| # Show the image | |
| plt.show() |
A imagem abaixo mostra o script aberto no editor Notepad++:

Obs: Na imagem exemplo acima o Notepad++ foi configurado para um estilo de cores escuras, chamado “Obsidian”, em “Configurações” > “Configurador de estilos” > “Selecionar tema:” > “Obsidian”. Isto é completamente opcional. Voltemos ao script.
Basicamente, na linha 10 especificamos o arquivo NetCDF que desejamos manipular, na linha 13, lemos o conteúdo do conjunto de dados chamado “analysed_sst” (os dados de TSM), na linha 16 configuramos o tamanho do nosso plot (10×5 polegadas neste exemplo), na linha 19 configuramos a aparência do nosso plot (temperaturas mínimas, máximas, origem do dado e paleta de cores) e na linha 22 salvamos o plot no formato PNG. Já na linha 25, mostramos o plot numa janela interativa.
O mais importante para entendermos nesse primeiro script é a seguinte linha:
# Extract the Sea Surface Temperature
data = file.variables['analysed_sst'][0,:,:]
Nela, estamos indicando que desejamos ler o “dataset” de TSM disponível nesse NetCDF, chamado “analysed_sst”. Esse dado é uma matriz de 3 dimensões, sendo: data, linhas e colunas. Neste arquivo em específico, temos apenas uma data disponível, portanto nossa matriz 3d tem apenas uma camada. Por isso indicamos o índice “0” no primeiro campo. Já nos outros dois, utilizamos dois pontos “:”, indicando que desejamos ler toda a matriz de linhas e colunas, ou seja, todo o dado global. No Script 6 deste procedimento vamos verificar como ler apenas uma região específica.
De momento, vamos apenas executar o script. No “Anaconda Prompt”, com o ambiente virtual “ocean” ativado…
conda activate open
…acesse o diretório C:\VLAB\Python\ (ou o seu diretório de trabalho):
cd C:\VLAB\Python
Execute o script “script_01.py” com o seguinte comando:
python script_01.py
A imagem abaixo mostra o procedimento acima:

Ao executar o script_01.py, veremos o plot resultante em uma janela interativa:

Ao mover o ponteiro do mouse sobre o plot, no canto superior direito você pode visualizar a linha e coluna correspondente, além dos valores de TSM (°C) de um pixel específico.

Vamos adicionar algumas informações ao plot no nosso próximo script!
SCRIPT 2: LENDO METADADOS E ADICIONANDO LEGENDA, TÍTULO E DATA
Vamos criar nosso segundo script e plotar uma imagem com mais informações sobre o dado. Crie e salve um arquivo chamado “script_02.py”.
Neste exemplo vamos ler a data do arquivo diretamente de seus metadados. Porém, como vamos ver no curso, o arquivo possui a seguinte informação relacionada à data: “segundos desde 01/01/1981 00:00 UTC”. Precisaremos somar esta quantidade de segundos à esta data inicial para calcular a data de aquisição. O Python facilita a manipulação desse tipo de informação (datas e horários) através da biblioteca “datetime”, que vamos importar neste segundo script na seguinte linha:
from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy
O fragmento de código abaixo mostra o comando para adicionar uma legenda, os comandos para calcular a data do arquivo e os comandos para adicionar um título ao plot (os comandos serão explicados durante o curso):
# Add a colorbar
plt.colorbar(label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05)
# Getting the file time and date
add_seconds = int(file.variables['time'][0])
date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds)
date_formatted = date.strftime('%Y-%m-%d')
# Add a title
plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left')
plt.title('INPE / CGCT / DISSM', fontsize=10, loc='right')
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 2: Reading the Metadate, Adding a Legend, Title and Date | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(10,5)) | |
| # Plot the image | |
| plt.imshow(data, vmin=-2, vmax=35, origin='lower', cmap='jet') | |
| # Add a colorbar | |
| plt.colorbar(label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left') | |
| plt.title('INPE / CGCT / DISSM', fontsize=10, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_02.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_02.py” com o seguinte comando:
python script_02.py
Ao executar o script, aparecerá uma nova janela com o nosso plot, já com os títulos e legendas adicionados:

Até o momento nosso dado está sendo plotado mostrando as informações em linhas e colunas (3600 linhas x 7200 colunas), isso porque não georreferenciamos nossa imagem. No terceiro exemplo, vamos utilizar a biblioteca Cartopy para adicionar mapas e outras informações ao nosso plot.
SCRIPT 3: ADICIONANDO MAPAS COM A CARTOPY
Crie e salve um arquivo chamado “script_03.py”.
Vamos importar a bilbioteca cartopy (para adicionar mapas entre outras características) e a biblioteca numpy (para facilitar algumas operações) com as seguintes linhas:
import cartopy, cartopy.crs as ccrs # Plot maps
import cartopy.feature as cfeature # Common drawing and filtering operations
import numpy as np # Import the Numpy package
Como vamos ver, precisamos informar à biblioteca Cartopy qual a extensão do nosso dado (latitudes e longitudes mínimas e máximas). Para isso vamos ler pela primeira vez as matrizes de latitudes e longitudes do nosso dado:
# Reading the lats and lons
lats = file.variables['lat'][:]
lons = file.variables['lon'][:]
O primeiro passo para usar a Cartopy é informar a projeção desejada (no exemplo abaixo, “PlateCaree”, ou cilíndrica equidistante) e informar qual são os limites geográficos do nosso plot:
# Use the Cilindrical Equidistant projection in cartopy
ax = plt.axes(projection=ccrs.PlateCarree())
# Define the image extent
img_extent = [lons.min(), lons.max(), lats.min(), lats.max()]
Após isso, podemos adicionar as linhas de costa, países, linhas de referência de latitudes e longitudes, além de uma máscara de continentes (pois não há dados nessas regiões):
# Add coastlines, borders and gridlines
ax.coastlines(resolution='50m', color='black', linewidth=0.8)
ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5)
gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 30), ylocs=np.arange(-90, 90, 10), draw_labels=True)
gl.top_labels = False
gl.right_labels = False
# Add a land mask
ax.add_feature(cfeature.LAND)
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 3: Adding Maps with Cartopy | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import numpy as np # Import the Numpy package | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| # Reading the lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(13,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [lons.min(), lons.max(), lats.min(), lats.max()] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 30), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Add a land mask | |
| ax.add_feature(cfeature.LAND) | |
| # Plot the image | |
| img = ax.imshow(data, vmin=-2, vmax=35, origin='lower', extent=img_extent, cmap='jet') | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left') | |
| plt.title('INPE / CGCT / DISSM', fontsize=10, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_03.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_03.py” com o seguinte comando:
python script_03.py
Ao executar o script, aparecerá uma nova janela com o nosso plot, já com os mapas adicionados:

Veja que agora, ao mover o ponteiro do mouse sobre o plot, além das temperaturas, vemos as coordenadas de cada ponto.

Uma das características da biblioteca Cartopy é a possibilidade de mudar a projeção do plot, o que pode ser útil em alguns casos. Muitos produtos encontrados nas páginas da NOAA são mostrados na projeção Mercator por exemplo. Vamos fazer alguns testes no nosso quarto script:
SCRIPT 4: MODIFICANDO A PROJEÇÃO DO PLOT
Crie e salve um arquivo chamado “script_04.py”.
No seguinte link, podemos ver as projeções disponíveis da Cartopy:
Nesta atividade vamos testar três projeções: Mercator, Robinson e Mollweide.
As únicas modificações em relação ao script anterior, é a declaração da projeção utilizada e a declaração da região, conforme o exemplo abaixo:
# Use the Mercator projection in cartopy
ax = plt.axes(projection=ccrs.Mollweide(central_longitude=0.0))
# Method used for "global" plots
ax.set_global()
Na segunda instrução estamos dizendo que este é um dado global, o que simplifica um pouco o nosso script.
Também vamos adicionar uma imagem de fundo (uma das opções padrão da Cartopy), ao invés da máscara de continentes:
# Add a background map
ax.stock_img()
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 4.1: Cartopy Projections (Mercator) | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import numpy as np # Import the Numpy package | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(8,8)) | |
| # Use the Mercator projection in cartopy | |
| ax = plt.axes(projection=ccrs.Mercator(central_longitude=0.0)) | |
| # Method used for "global" plots | |
| ax.set_global() | |
| # Add a background map | |
| ax.stock_img() | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 30), ylocs=np.arange(-90, 90, 10), draw_labels=False) | |
| # Plot the image | |
| plt.imshow(data, vmin=-2, vmax=35, origin='lower', cmap='jet', transform=ccrs.PlateCarree()) | |
| # Add a colorbar | |
| plt.colorbar(label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left') | |
| plt.title('Mercator Projection', fontsize=10, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_04.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_04.py” com o seguinte comando:
python script_04.py
Ao executar o script, aparecerá uma nova janela com o nosso plot, na projeção configurada (Mercator neste caso):

Agora vamos testar outras projeções. Por ser um dado global as modificações são bem simples. Mude a linha 23 de “Mercator” para “Robinson”:
# Use the Robinson projection in cartopy
ax = plt.axes(projection=ccrs.Robinson(central_longitude=0.0))
Mude também o subtítulo do plot:
plt.title('Robinson Projection', fontsize=10, loc='right')
E mude o tamanho do plot para 13 x 7 polegadas:
# Choose the plot size (width x height, in inches)
plt.figure(figsize=(13,7))
Execute o script 4 novamente:
python script_04.py
Você verá o mesmo plot, agora na projeção Robinson:

Modifique agora a projeção para “Mollweide”:
# Use the Mollweide projection in cartopy
ax = plt.axes(projection=ccrs.Mollweide(central_longitude=0.0))
E execute o script novamente. Você verá o plot na projeção Mollweide:

Com estas simples modificações, podemos alterar a projeção do nosso plot. Nossos plots já estão bem interessantes, porém alguns detalhes podem ser melhorados. No nosso próximo script, vamos ver como criar paletas de cores personalizadas.
SCRIPT 5: PALETAS DE CORES PERSONALIZADAS
Crie e salve um arquivo chamado “script_05.py”.
Até o momento, estamos utilizando a paleta de cores “jet”, umas das opções padrão da matplotlib, que podem ser encontradas no seguinte link:
matplotlib.org/stable/tutorials/colors/colormaps.html
Apesar de variadas, nem sempre atendem as necessidades do plot, sendo necessário por vezes criarmos paletas de cores personalizadas. É possível criar paletas de cores com qualquer número de cores, com qualquer cor ou combinação de cores. Vamos ver dois exemplo, um com uma escala contínua e outra discreta.
Vamos reproduzir a paleta de cores de TSM encontrada na página Worldview da NASA, que pode ser visualizada neste link. Esta é uma paleta de intervalos contínuos, que não consta nas paletas padrão da matplotlib.
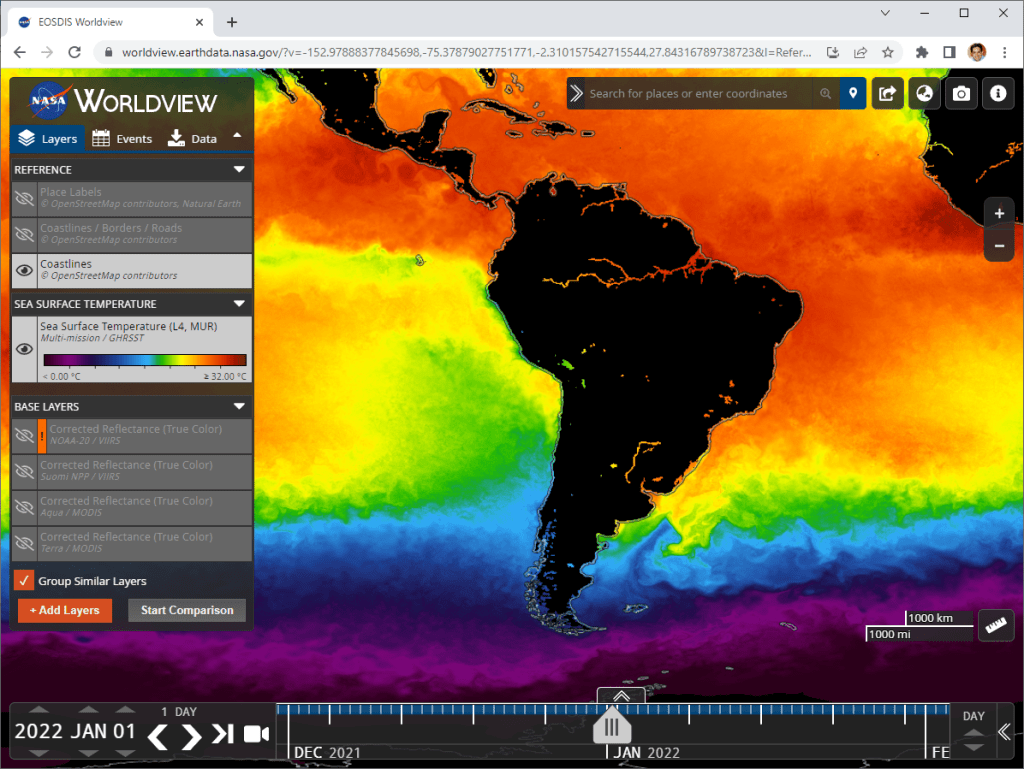
Como esta paleta não está disponível na lista de colormaps padrão da matplotlib, para reproduzi-la, precisamos especificar via código a representação de cada intervalo de cores, porém em hexadecimal. Como podemos fazer isso?
Não é difícil. Vamos acessar a seguinte página:
https://imagecolorpicker.com/
Esta página possibilita extrairmos os valores das cores de uma imagem de referência.
Na página, clique no botão “Use Your Image”:

Na próxima janela, selecione a aba “Website Url” e cole o endereço da página de interesse, como o link do Worldview informado mais acima. Clique “OK”.

A página tirará um printscreen automaticamente e você pode clicar em qualquer ponto da imagem da página para verificar o valor hexadecimal das cores, podendo assim utilizar estes valores nos scripts.
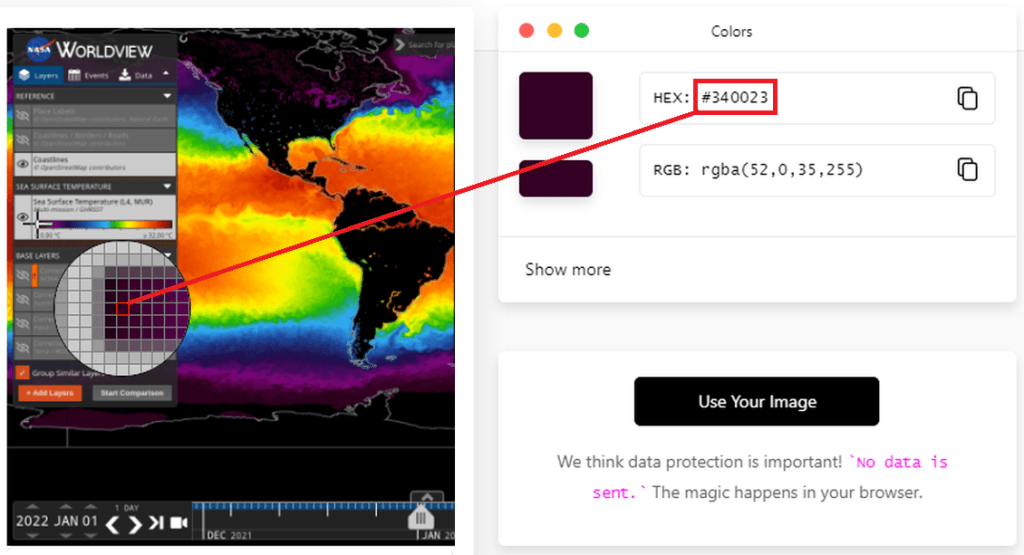
Agora vamos inserir os valores hexadecimais no nosso script e criar uma paleta de cores personalizada. Primeiramente, vamos importar o módulo “colors” da matplotlib, necessário para essa operação:
import matplotlib.colors # Matplotlib colors
No exemplo, foram obtidas através da página “imagecolorpicker” 18 amostras de cores da escala do Worldview (clicando em intervalos espaçados da mesma). Além disso, especificamos a cor que será atribuída aos valores acima do limite superior e uma cor que será atribuída aos valores abaixo do limite inferior (sendo as mesmos valores hexadecimais do 1° valor e 18° valor da lista, neste exemplo).
O código abaixo mostra as cores já em hexadecimal, e as demais instruções necessárias para criar a paleta de valores contínuos. As cores do intervalo entre os valores hexadecimais informados, serão criados automaticamente pela função “LinearSegmentColormap” da matplotlib.
# Create a custom color scale:
# Reference color scale from NASA Wordview: https://worldview.earthdata.nasa.gov/
# HEX values got from: https://imagecolorpicker.com/:
colors = ["#2d001c", "#5b0351", "#780777", "#480a5e", "#1e1552",
"#1f337d", "#214c9f", "#2776c6", "#2fa5f1", "#1bad1d",
"#8ad900", "#ffec00", "#ffab00", "#f46300", "#de3b00",
"#ab1900", "#6b0200", '#3c0000']
cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors)
cmap.set_over('#3c0000')
cmap.set_under('#2d001c')
vmin = -2.0
vmax = 35.0
Também, no nosso script precisamos informar na instrução “imshow” a paleta de cores (que chamamos “cmap”) criada acima:
# Plot the image
img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap)
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 5: Custom Color Palettes | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import numpy as np # Import the Numpy package | |
| import matplotlib.colors # Matplotlib colors | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| # Reading the lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(13,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [lons.min(), lons.max(), lats.min(), lats.max()] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 30), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Create a custom color scale: | |
| # Reference color scale from NASA Wordview: https://worldview.earthdata.nasa.gov/ | |
| # HEX values got from: https://imagecolorpicker.com/: | |
| colors = ["#2d001c", "#5b0351", "#780777", "#480a5e", "#1e1552", | |
| "#1f337d", "#214c9f", "#2776c6", "#2fa5f1", "#1bad1d", | |
| "#8ad900", "#ffec00", "#ffab00", "#f46300", "#de3b00", | |
| "#ab1900", "#6b0200", '#3c0000'] | |
| cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors) | |
| cmap.set_over('#3c0000') | |
| cmap.set_under('#2d001c') | |
| vmin = -2.0 | |
| vmax = 35.0 | |
| # Add a land mask | |
| ax.add_feature(cfeature.LAND) | |
| # Plot the image | |
| img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap) | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left') | |
| plt.title('INPE / CGCT / DISSM', fontsize=10, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_05.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_05.py” com o seguinte comando:
python script_05.py
Ao executar o script, aparecerá uma nova janela com o nosso plot, com a nova paleta de cores criada via código:

Ao compararmos com o NASA Worldview para a mesma data (01/01/2022 neste exemplo), obtivemos o mesmo resultado:

Agora vamos criar uma paleta de cores de intervalos discretos, utilizando como referência a seguinte paleta da NOAA, que possui 17 cores (com exceção do branco):


Vamos colocar o seguinte link na página “imagecolorpicker.com” para que a página faça um printscreen automático:
psl.noaa.gov/map/images/sst/sst.daily.gif
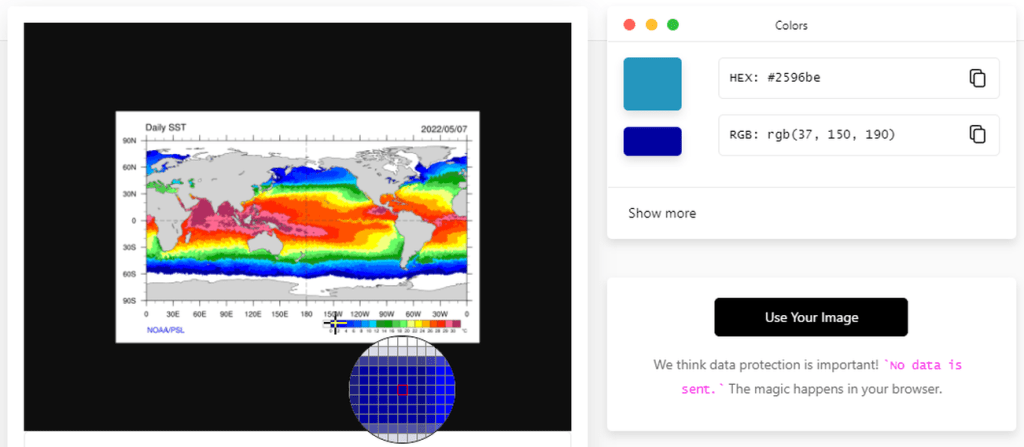
E verificar os 17 valores hexadecimal desta escala de cores:
# Create a custom color scale:
# Reference color scale from NASA Wordview: https://psl.noaa.gov/map/clim/sst.shtml
# HEX values got from: https://imagecolorpicker.com/:
colors = ["#0000a1", "#0000fe", "#0034ff", "#0356fc", "#0199fc",
"#01daff", "#238e25", "#00a001", "#4bcc4e", "#62fe64",
"#f5fe81", "#ffff02", "#ffb200", "#fd5106", "#ff2600",
"#fb6a94", "#b52c64"]
cmap = matplotlib.colors.ListedColormap(colors)
cmap.set_over('#b52c64')
cmap.set_under('#0000a1')
vmin = 0.0
vmax = 34.0
O que muda da escala contícua para a discreta é o seguinte comando que de “LinearSegmentedColormap”:
cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors)
Muda para “ListedColormap”:
cmap = matplotlib.colors.ListedColormap(colors)
Além disso, vamos especificar na legenda os valores que desejamos mostrar. Para que esses valores batam com as divisões, precisamos ter o número de cores da escala + 2 valores. Neste exemplo, temos 19 valores (17 cores da escala criada + 2 valores). Também, adicionamos o parâmetro “ticks” à instrução “colorbar”:
# Define the ticks to be shown
ticks = [-2, 0, 2, 4, 6, 8, 10, 12, 14, 16, 18, 20, 22, 24, 26, 28, 30, 32, 34]
# Add a colorbar
plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05, ticks=ticks)
Abaixo, o script completo com a paleta com valores discretos:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 5.2: Custom Color Palettes (Discrete) | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import numpy as np # Import the Numpy package | |
| import matplotlib.colors # Matplotlib colors | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][0,:,:] | |
| # Reading the lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(13,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [lons.min(), lons.max(), lats.min(), lats.max()] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 30), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Create a custom color scale: | |
| # Reference color scale from NOAA: https://psl.noaa.gov/map/clim/sst.shtml | |
| # HEX values got from: https://imagecolorpicker.com/: | |
| colors = ["#0000a1", "#0000fe", "#0034ff", "#0356fc", "#0199fc", | |
| "#01daff", "#238e25", "#00a001", "#4bcc4e", "#62fe64", | |
| "#f5fe81", "#ffff02", "#ffb200", "#fd5106", "#ff2600", | |
| "#fb6a94", "#b52c64"] | |
| cmap = matplotlib.colors.ListedColormap(colors) | |
| cmap.set_over('#b52c64') | |
| cmap.set_under('#0000a1') | |
| vmin = 0.0 | |
| vmax = 34.0 | |
| # Add a land mask | |
| ax.add_feature(cfeature.LAND) | |
| # Plot the image | |
| img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap) | |
| # Define the ticks to be shown | |
| ticks = [-2, 0, 2, 4, 6, 8, 10, 12, 14, 16, 18, 20, 22, 24, 26, 28, 30, 32, 34] | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='horizontal', pad=0.05, fraction=0.05, ticks=ticks) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=10, loc='left') | |
| plt.title('INPE / CGCT / DISSM', fontsize=10, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_05b.png') | |
| # Show the image | |
| plt.show() |
Ao executar o script, vemos o mesmo plot, agora com a paleta de cores discreta:

Veja que os valores selecionados na lista “ticks” batem exatamente com os intervalos da paleta de cores criada via código.
Até o momento, estamos plotando a imagem em toda sua extensão global. No próximo exemplo, vamos verificar como plotar apenas uma região específica do dado.
SCRIPT 6: PLOTANDO UMA REGIÃO ESPECÍFICA
Crie e salve um arquivo chamado “script_06.py”.
Até o momento, estamos lendo o dado de TSM do seguinte modo:
# Extract the Sea Surface Temperature
data = file.variables['analysed_sst'][0,:,:]
Esta é uma matriz de 3 dimensões (data, linhas e colunas), sendo que para este dado em específico temos apenas uma data no arquivo, portanto sempre utilizamos o índice “0” no primeiro item entre colchetes (é uma matriz 3d de camada única). Já nos outros dois campos, utilizamos dois pontos “:”, indicando que desejamos ler a matriz completa de linhas e colunas (3600 linhas x 7200 colunas), ou seja, o dado global.
Para lermos apenas os dados de uma região específica do globo, precisamos saber exatamente quais são os índices iniciais e finais das linhas e colunas que correspondem as coordenadas desejadas. Felizmente, nosso dado NetCDF possui matrizes de latitudes e longitudes, das quais podemos extrair os índices de interesse. Precisamos de 4 índices: longitude mínima, longitude máxima, latitude mínima e latitude máxima. Com esses 4 índices, podemos ler o dados apenas para a região de interesse.
Vamos ver como fazer.
O primeiro passo é indicar no script qual a região de interesse. No exemplo abaixo estamos criando uma lista de coordenadas chamada “extent”, e declarando quatro valores (longitude mínima, latitude mínima, longitude máxima, latitude máxima). No exemplo abaixo temos os valores para a região aproximada da América do Sul.
# Select the extent [min. lon, min. lat, max. lon, max. lat]
extent = [-93.0, -60.00, -25.00, 18.00] # South America
Também, vimos em um script anterior a possibilidade de extrairmos os valores de latitudes e longitudes do nosso dado utilizando os seguintes comandos:
# Reading the lats and lons
lats = file.variables['lat'][:]
lons = file.variables['lon'][:]
Com a região desejada e as matrizes de latitude e longitude armazenadas, podemos encontrar os índices de nosso dado, do seguinte modo:
# Latitude lower and upper index
latli = np.argmin( np.abs( lats - extent[1] ) )
latui = np.argmin( np.abs( lats - extent[3] ) )
# Longitude lower and upper index
lonli = np.argmin( np.abs( lons - extent[0] ) )
lonui = np.argmin( np.abs( lons - extent[2] ) )
Basicamente, estamos subtraindo as coordenadas desejadas (“extent”) das nossas matrizes de latitudes e longitudes (“lats” e “lons”). Após essa subtração, encontramos os índices desejados com a função numpy “argmin”, que retorna o índice do menor valor encontrado. Se por exemplo, declarei uma longitude mínima de -93°, ao subtrair 93 de minha matriz “lons”, a posição (ou índice) que estiver mais próximo de -93°, será o índice retornado pelo “np.argmin”, pois o valor da subtração será igual ou estará próximo de 0. Meio complicado, mas explicaremos com mais detalhes no treinamento.
Com os 4 índices calculados, vamos ler a nossa matriz de dados novamente, porém, apenas a região de interesse:
# Extract the Sea Surface Temperature
data = file.variables['analysed_sst'][ 0 , latli:latui , lonli:lonui ]
Estamos dizendo que desejamos apenas os dados que estejam entre os índices mínimos e máximos de latitude e mínimos e máximos de longitude.
Após isso, precisamos dizer para a Cartopy qual é nossa região de interesse:
# Use the Cilindrical Equidistant projection in cartopy
ax = plt.axes(projection=ccrs.PlateCarree())
ax.set_extent([extent[0], extent[2], extent[1], extent[3]], ccrs.PlateCarree())
# Define the image extent
img_extent = [extent[0], extent[2], extent[1], extent[3]]
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 6: Plotting a Specific Region | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import numpy as np # Import the Numpy package | |
| import matplotlib.colors # Matplotlib colors | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Select the extent [min. lon, min. lat, max. lon, max. lat] | |
| extent = [-93.0, -60.00, -25.00, 18.00] # South America | |
| # Reading lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| # Latitude lower and upper index | |
| latli = np.argmin( np.abs( lats - extent[1] ) ) | |
| latui = np.argmin( np.abs( lats - extent[3] ) ) | |
| # Longitude lower and upper index | |
| lonli = np.argmin( np.abs( lons - extent[0] ) ) | |
| lonui = np.argmin( np.abs( lons - extent[2] ) ) | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][ 0 , latli:latui , lonli:lonui ] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(7,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| ax.set_extent([extent[0], extent[2], extent[1], extent[3]], ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [extent[0], extent[2], extent[1], extent[3]] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 10), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Create a custom color scale: | |
| # Reference color scale from NASA Wordview: https://worldview.earthdata.nasa.gov/ | |
| # HEX values got from: https://imagecolorpicker.com/: | |
| colors = ["#2d001c", "#5b0351", "#780777", "#480a5e", "#1e1552", | |
| "#1f337d", "#214c9f", "#2776c6", "#2fa5f1", "#1bad1d", | |
| "#8ad900", "#ffec00", "#ffab00", "#f46300", "#de3b00", | |
| "#ab1900", "#6b0200", '#3c0000'] | |
| cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors) | |
| cmap.set_over('#3c0000') | |
| cmap.set_under('#2d001c') | |
| vmin = -2.0 | |
| vmax = 35.0 | |
| # Add a land mask | |
| ax.add_feature(cfeature.LAND) | |
| # Plot the image | |
| img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap) | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='vertical', pad=0.05, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=7, loc='left') | |
| plt.title('Region: ' + str(extent), fontsize=7, loc='right') | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_06.png') | |
| # Show the image | |
| plt.show() |
Veja que alteramos também o tamanho do plot e o subtítulo e mudamos a barra de cores para vertical.
Execute o script “script_06.py” com o seguinte comando:
python script_06.py
Ao executar o script, veremos apenas a região de interesse sendo plotada.

Vamos adicionar ao nosso plot alguns itens adicionais, como shapefiles e textos.
SCRIPT 7: ADICIONANDO SHAPEFILES E TEXTOS
Crie e salve um arquivo chamado “script_07.py”.
Agora que já sabemos plotar uma região específica, vamos adicionar algumas decorações aos nossos plots. Neste exemplo, vamos adicionar dois shapefiles, um de estados e províncias mundiais, e outro da METAREA V (área de responsabilidade de Brasil perante a OMM, para a qual o Serviço Meteorológico Marinho emite avisos de mau tempo e previsões meteorológicas aos navegantes e toda a comunidade marítima). Além disso, vamos adicionar alguns textos indicando as subregiões da METAREA V e um texto adicional, dentro de uma caixa, no canto inferior direito do plot.
Antes de criar os scripts, vamos baixar os shapefiles e colocá-los no nosso diretório de trabalho.
O shapefile de estados e províncias mundiais pode ser baixado no seguinte link:
O shapefile da METAREA V pode ser baixado no seguinte link:
O conteúdo do nosso diretório de trabalho nesse momento será:

Extraia os dois arquivos “.zip” dos shapefiles no diretório de trabalho, para que possamos utilizá-los no nosso script.
O primeiro passo para adicionar shapefiles ao nosso plot é importar o módulo “shapereader” da biblioteca Cartopy:
import cartopy.io.shapereader as shpreader # Import shapefiles
Com ele, podemos importar os dois shapefiles ao nosso plot:
# Add a shapefile
shapefile = list(shpreader.Reader('ne_10m_admin_1_states_provinces.shp').geometries())
ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='gray',facecolor='none', linewidth=0.3)
# Add a shapefile
shapefile = list(shpreader.Reader('Metareas.shp').geometries())
ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='black',facecolor='none', linewidth=1.0)
Na instrução “shpreader.Reader” indicamos o nome dos arquivos “.shp” que foram extraídos dos arquivos “.zip”, no nosso caso ‘ne_10m_admin_1_states_provinces.shp’ e ‘Metareas.shp’. Também indicamos a cor no parâmetro “edgecolor” e a espessura da linha no parâmetro “linewidth”.
De acordo com a OMM, na METAREA V nos temos algumas sub-regiões (chamadas de “Forecast Areas”, conforme imagem abaixo:

O nosso shapefile da METAREA V que estamos utilizando não contém as nomenclaturas de cada sub-região, então vamos adicioná-las via código. Será um bom exemplo de como adicionar anotações ao nosso plot. Vamos utilizar o seguinte código:
# Add texts
txt1 = ax.annotate("METAREA V", xy=(-28, 9), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt2 = ax.annotate("A", xy=(-48, -32), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt3 = ax.annotate("B", xy=(-43, -27), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt4 = ax.annotate("C", xy=(-46, -25), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt5 = ax.annotate("D", xy=(-38, -22), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt6 = ax.annotate("E", xy=(-36, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt7 = ax.annotate("F", xy=(-33, -10), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt8 = ax.annotate("G", xy=(-36, -2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt9 = ax.annotate("H", xy=(-46, 2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt10 = ax.annotate("N", xy=(-22, -13), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
txt11 = ax.annotate("S", xy=(-22, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree())
No primeiro parâmetro do comando “annotate” especificamos o texto desejado, já no parâmetro “xy” especificamos a posição do texto, neste caso, em coordenadas de longitude e latitude. Especificamos também a cor e seu tamanho, entre outros parâmetros.
E uma última anotação que adicionaremos ao nosso plot é um pequeno texto dentro de uma caixa no canto inferior direito, indicando algumas siglas do INPE:
# Add a text inside the plot
from matplotlib.offsetbox import AnchoredText
text = AnchoredText("INPE / CGCT / DISSM", loc=4, prop={'size': 7}, frameon=True)
ax.add_artist(text)
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 7: Adding Shapefiles and Texts | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import cartopy.io.shapereader as shpreader # Import shapefiles | |
| import numpy as np # Import the Numpy package | |
| import matplotlib.colors # Matplotlib colors | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Select the extent [min. lon, min. lat, max. lon, max. lat] | |
| extent = [-93.0, -60.00, -10.00, 18.00] # South America | |
| # Reading lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| # Latitude lower and upper index | |
| latli = np.argmin( np.abs( lats - extent[1] ) ) | |
| latui = np.argmin( np.abs( lats - extent[3] ) ) | |
| # Longitude lower and upper index | |
| lonli = np.argmin( np.abs( lons - extent[0] ) ) | |
| lonui = np.argmin( np.abs( lons - extent[2] ) ) | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][ 0 , latli:latui , lonli:lonui ] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(7,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| ax.set_extent([extent[0], extent[2], extent[1], extent[3]], ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [extent[0], extent[2], extent[1], extent[3]] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 10), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Create a custom color scale: | |
| colors = ["#2d001c", "#5b0351", "#780777", "#480a5e", "#1e1552", | |
| "#1f337d", "#214c9f", "#2776c6", "#2fa5f1", "#1bad1d", | |
| "#8ad900", "#ffec00", "#ffab00", "#f46300", "#de3b00", | |
| "#ab1900", "#6b0200", '#3c0000'] | |
| cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors) | |
| cmap.set_over('#3c0000') | |
| cmap.set_under('#28000a') | |
| vmin = -2.0 | |
| vmax = 35.0 | |
| # Add a background map | |
| ax.stock_img() | |
| # Plot the image | |
| img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap) | |
| # Add a shapefile | |
| shapefile = list(shpreader.Reader('ne_10m_admin_1_states_provinces.shp').geometries()) | |
| ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='gray',facecolor='none', linewidth=0.3) | |
| # Add a shapefile | |
| shapefile = list(shpreader.Reader('Metareas.shp').geometries()) | |
| ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='black',facecolor='none', linewidth=1.0) | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='vertical', pad=0.02, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=7, loc='left') | |
| plt.title('Region: ' + str(extent), fontsize=7, loc='right') | |
| # Add a text inside the plot | |
| from matplotlib.offsetbox import AnchoredText | |
| text = AnchoredText("INPE / CGCT / DISSM", loc=4, prop={'size': 7}, frameon=True) | |
| ax.add_artist(text) | |
| # Add texts | |
| txt1 = ax.annotate("METAREA V", xy=(-28, 9), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt2 = ax.annotate("A", xy=(-48, -32), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt3 = ax.annotate("B", xy=(-43, -27), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt4 = ax.annotate("C", xy=(-46, -25), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt5 = ax.annotate("D", xy=(-38, -22), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt6 = ax.annotate("E", xy=(-36, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt7 = ax.annotate("F", xy=(-33, -10), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt8 = ax.annotate("G", xy=(-36, -2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt9 = ax.annotate("H", xy=(-46, 2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt10 = ax.annotate("N", xy=(-22, -13), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt11 = ax.annotate("S", xy=(-22, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_07.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_07.py” com o seguinte comando:
python script_7.py
Ao executar o script, veremos os shapefiles e anotações adicionados ao nosso plot:

Para finalizar os exemplos do nosso procedimento pré-curso, vamos ver como adicionar o valor de TSM de um determinado pixel ao nosso plot, em uma caixa de texto estilizada.
SCRIPT 8: LENDO DADOS DE UMA COORDENADA E ADICIONANDO AO PLOT
Crie e salve um arquivo chamado “script_08.py”.
No script 6 vimos como plotar uma região específica, e para isso calculamos os índices de nossa região utilizando as matrizes de latitude e longitude. Neste exemplo vamos fazer algo semelhante, porém, ao invés de quatro índices como no script 6 (min lon, min lat, max lon e max lat), vamos calcular apenas dois, que serão nossos pontos de lat e lon desejados.
Faremos no seguinte modo:
# Reading the data from a coordinate
lat_point = -30
lon_point = -30
lat_idx = np.argmin(np.abs(lats - lat_point))
lon_idx = np.argmin(np.abs(lons - lon_point))
data_point = file.variables['analysed_sst'][ 0 , lat_idx , lon_idx ].round(2)
No exemplo acima, definimos uma coordenada específica (lat: -30° e lon: -30° neste caso), calculamos os índices mais próximos a esta coordenada e extraímos da nossa matriz de dados apenas este ponto. Além disso, arredondamos o resultado em duas casas decimais (.round(2)).
Após obter os dados de interesse na nossa matriz, adicionamos a informação a uma caixa de texto, do seguinte modo:
# Adding the data as an annotation
# Add a circle
ax.plot(lon_point, lat_point, 'o', color='red', markersize=5, transform=ccrs.Geodetic(), markeredgewidth=1.0, markeredgecolor=(0, 0, 0, 1))
# Add a text
txt_offset_x = 0.8
txt_offset_y = 0.8
plt.annotate("Lat: " + str(lat_point) + "\n" + "Lon: " + str(lon_point) + "\n" + "SST: \n" + str(data_point) + ' °C', xy=(lon_point + txt_offset_x, lat_point + txt_offset_y), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), fontsize=7, fontweight='bold', color='gold', bbox=dict(boxstyle="round",fc=(0.0, 0.0, 0.0, 0.5), ec=(1., 1., 1.)), alpha = 1.0)
Primeiro adicionamos um circulo na coordenada de interesse, definimos um “offset” (em graus) para a caixa de texto (para que ela não fique sobreposta ao círculo), e finalmente criamos a caixa de texto com o conteúdo desejado.
Assim como no script 7, no primeiro parâmetro da instrução “annotate” especificamos o texto, no segundo a posição, e nos demais a cor, tamanho entre outras características. A diferença em relação ao script 7, é que utilizamos o parâmetro “bbox”, onde definimos as características da caixa de texto.
Abaixo, o script completo até o momento:
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # INPE / CGCT / DISSM - Training: Oceanography Products - Script 8: Reading Data from a Coordinate and Adding it to the Plot | |
| # Author: Diego Souza (INPE / CGCT / DISSM) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Required modules | |
| from netCDF4 import Dataset # Read / Write NetCDF4 files | |
| import matplotlib.pyplot as plt # Plotting library | |
| from datetime import datetime, timedelta # Library to convert julian day to dd-mm-yyyy | |
| import cartopy, cartopy.crs as ccrs # Plot maps | |
| import cartopy.feature as cfeature # Common drawing and filtering operations | |
| import cartopy.io.shapereader as shpreader # Import shapefiles | |
| import numpy as np # Import the Numpy package | |
| import matplotlib.colors # Matplotlib colors | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Open the file using the NetCDF4 library | |
| file = Dataset("coraltemp_v3.1_20220101.nc") | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Select the extent [min. lon, min. lat, max. lon, max. lat] | |
| extent = [-93.0, -60.00, -10.00, 18.00] # South America | |
| # Reading lats and lons | |
| lats = file.variables['lat'][:] | |
| lons = file.variables['lon'][:] | |
| # Latitude lower and upper index | |
| latli = np.argmin( np.abs( lats - extent[1] ) ) | |
| latui = np.argmin( np.abs( lats - extent[3] ) ) | |
| # Longitude lower and upper index | |
| lonli = np.argmin( np.abs( lons - extent[0] ) ) | |
| lonui = np.argmin( np.abs( lons - extent[2] ) ) | |
| # Extract the Sea Surface Temperature | |
| data = file.variables['analysed_sst'][ 0 , latli:latui , lonli:lonui ] | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Choose the plot size (width x height, in inches) | |
| plt.figure(figsize=(7,7)) | |
| # Use the Cilindrical Equidistant projection in cartopy | |
| ax = plt.axes(projection=ccrs.PlateCarree()) | |
| ax.set_extent([extent[0], extent[2], extent[1], extent[3]], ccrs.PlateCarree()) | |
| # Define the image extent | |
| img_extent = [extent[0], extent[2], extent[1], extent[3]] | |
| # Add coastlines, borders and gridlines | |
| ax.coastlines(resolution='50m', color='black', linewidth=0.8) | |
| ax.add_feature(cartopy.feature.BORDERS, edgecolor='black', linewidth=0.5) | |
| gl = ax.gridlines(crs=ccrs.PlateCarree(), color='white', alpha=1.0, linestyle='--', linewidth=0.25, xlocs=np.arange(-180, 180, 10), ylocs=np.arange(-90, 90, 10), draw_labels=True) | |
| gl.top_labels = False | |
| gl.right_labels = False | |
| # Create a custom color scale: | |
| colors = ["#2d001c", "#5b0351", "#780777", "#480a5e", "#1e1552", | |
| "#1f337d", "#214c9f", "#2776c6", "#2fa5f1", "#1bad1d", | |
| "#8ad900", "#ffec00", "#ffab00", "#f46300", "#de3b00", | |
| "#ab1900", "#6b0200", '#3c0000'] | |
| cmap = matplotlib.colors.LinearSegmentedColormap.from_list("", colors) | |
| cmap.set_over('#3c0000') | |
| cmap.set_under('#28000a') | |
| vmin = -2.0 | |
| vmax = 35.0 | |
| # Add a background map | |
| ax.stock_img() | |
| # Plot the image | |
| img = ax.imshow(data, vmin=vmin, vmax=vmax, origin='lower', extent=img_extent, cmap=cmap) | |
| # Add a shapefile | |
| shapefile = list(shpreader.Reader('ne_10m_admin_1_states_provinces.shp').geometries()) | |
| ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='gray',facecolor='none', linewidth=0.3) | |
| # Add a shapefile | |
| shapefile = list(shpreader.Reader('Metareas.shp').geometries()) | |
| ax.add_geometries(shapefile, ccrs.PlateCarree(), edgecolor='black',facecolor='none', linewidth=1.0) | |
| # Add a colorbar | |
| plt.colorbar(img, label='Sea Surface Temperature (°C)', extend='both', orientation='vertical', pad=0.02, fraction=0.05) | |
| # Getting the file time and date | |
| add_seconds = int(file.variables['time'][0]) | |
| date = datetime(1981,1,1,0) + timedelta(seconds=add_seconds) | |
| date_formatted = date.strftime('%Y-%m-%d') | |
| # Add a title | |
| plt.title(f'NOAA Coral Reef Watch Daily 5 km SST - {date_formatted}', fontweight='bold', fontsize=7, loc='left') | |
| plt.title('Region: ' + str(extent), fontsize=7, loc='right') | |
| # Add a text inside the plot | |
| from matplotlib.offsetbox import AnchoredText | |
| text = AnchoredText("INPE / CGCT / DISSM", loc=4, prop={'size': 7}, frameon=True) | |
| ax.add_artist(text) | |
| # Add texts | |
| txt1 = ax.annotate("METAREA V", xy=(-28, 9), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt2 = ax.annotate("A", xy=(-48, -32), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt3 = ax.annotate("B", xy=(-43, -27), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt4 = ax.annotate("C", xy=(-46, -25), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt5 = ax.annotate("D", xy=(-38, -22), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt6 = ax.annotate("E", xy=(-36, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt7 = ax.annotate("F", xy=(-33, -10), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt8 = ax.annotate("G", xy=(-36, -2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt9 = ax.annotate("H", xy=(-46, 2), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt10 = ax.annotate("N", xy=(-22, -13), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| txt11 = ax.annotate("S", xy=(-22, -17), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), color='black', size=10, clip_on=True, annotation_clip=True, horizontalalignment='center', verticalalignment='center', transform=ccrs.PlateCarree()) | |
| # Reading the data from a coordinate | |
| lat_point = -30 | |
| lon_point = -30 | |
| lat_idx = np.argmin(np.abs(lats - lat_point)) | |
| lon_idx = np.argmin(np.abs(lons - lon_point)) | |
| data_point = file.variables['analysed_sst'][ 0 , lat_idx , lon_idx ].round(2) | |
| # Adding the data as an annotation | |
| # Add a circle | |
| ax.plot(lon_point, lat_point, 'o', color='red', markersize=5, transform=ccrs.Geodetic(), markeredgewidth=1.0, markeredgecolor=(0, 0, 0, 1)) | |
| # Add a text | |
| txt_offset_x = 0.8 | |
| txt_offset_y = 0.8 | |
| plt.annotate("Lat: " + str(lat_point) + "\n" + "Lon: " + str(lon_point) + "\n" + "SST: \n" + str(data_point) + ' °C', xy=(lon_point + txt_offset_x, lat_point + txt_offset_y), xycoords=ccrs.PlateCarree()._as_mpl_transform(ax), fontsize=7, fontweight='bold', color='gold', bbox=dict(boxstyle="round",fc=(0.0, 0.0, 0.0, 0.5), ec=(1., 1., 1.)), alpha = 1.0) | |
| #--------------------------------------------------------------------------------------------------------------------------- | |
| # Save the image | |
| plt.savefig('image_08.png') | |
| # Show the image | |
| plt.show() |
Execute o script “script_08.py” com o seguinte comando:
python script_08.py
Ao executar o script, veremos o valor da TSM para a coordenada de interesse adicionada ao plot:

Com este script nós terminamos as atividades pré-curso! Nesta atividade vimos alguns dos scripts básicos para manipulação de dados de TSM. Durante o curso, nós faremos uma revisão destes scripts e veremos novos scripts com novas operações para uma variedade de dados!
ACESSO AOS SCRIPTS DO PRÉ-CURSO E DURANTE O CURSO ONLINE
Encontre os scripts vistos na atividade pré-curso no link abaixo:
No curso veremos aproximadamente 30 scripts, que serão disponibilizados no link acima.